Application of TOPKAT and TEST software in prediction of chemical toxicity
-
+ English摘要:目的
归纳TOPKAT、TEST两款毒性预测软件对有毒化学物健康和生态毒性的可预测性和适用范围, 探讨高效、简便、快速的毒物检测实用方法。
方法采用简化分子线性输入规范(SMILES), 结合两款毒性预测软件对化学物的毒理学进行预测, 并将预测结果与欧洲化学品管理署公布的毒理学数据进行对比, 总结两款软件的优缺点。
结果TOPKAT和TEST软件能预测大多数的常见化学物毒性, TEST软件的化学物预测覆盖率高于TOPKAT软件, 能预测多取代苯环类、杂环类和大分子化学物, 而TOPKAT无法预测吡啶类、部分苯酚类和苯胺类化学物的毒性。两款毒性预测软件在预测化学物是否具有毒性方面的正确率均在85%左右。TOPKAT软件对于农药类化学物的毒性预测正确率高于TEST软件, TOPKAT预测值与文献值的线性决定系数R2为0.852(健康毒性)(P < 0.01)、0.826(生态毒性)(P < 0.01)。而TEST软件对于苯系化学物的毒性预测结果略优于TOPKAT软件, TEST预测值与文献值的线性决定系数R2为0.932(P < 0.01)(健康毒性)、0.787(生态毒性)(P < 0.01)。对于酯类和醇类化学物, TOPKAT和TEST软件都显示出良好的预测能力, 预测值与文献值的线性决定系数R2为0.854~0.986(健康毒性)(P < 0.01)、0.821~0.981(生态毒性)(P < 0.01)。
结论TOPKAT、TEST软件能高效、正确地预测大部分化学物的健康和生态毒性, 可为新化学物的健康和生态毒性评价提供依据, 为药物的早期开发提供决策支持。
-
化学物的健康和生态毒性关乎人身、财产和环境安全,还直接影响到生产、使用、经营、运输和仓储等环节。因此,化学物的毒性评估是非常重要的安全性评价内容。另外,由于环境污染事件频发,化学物的生态毒理性评价引起人们广泛的关注。传统的毒理学研究以动物实验为基础,存在周期长、成本高、灵敏度低等诸多弊端。近年来,以现代分析化学及化学物毒理学研究的实验数据和理论为基础,结合计算机技术和信息科学,人们采用多学科的交叉理论和技术对毒理学实验数据进行分析、研究和归纳,发掘了定量构效关系(quantitative structure-activity relationship,QSAR)模型,开发了相应的毒性预测方法[1-3]。它们具有快速、高效、经济、不依赖实验条件等优点,能为新化学物的健康和生态毒性评价提供参考依据。
目前,很多QSAR软件已经开发出来,并在健康和环境毒理学方面得到了广泛应用。例如,ECOSAR软件[4-5]、DEREK软性[6-7]、TOXTREE软件[8]、ACD/Labs软件、TEST软件和TOPKAT软件等[9]。其中,TOPKAT软件是应用最为广泛的毒性预测软件之一,TEST软件是最受推崇的免费毒性预测软件。TOPKAT和TEST软件能同时预测健康和生态毒性,并给出具体的毒性预测数值,而其他软件只能预测毒性程度。除了能预测口服毒性数据外,TOPKAT还能预测大鼠吸入毒性(半数致死浓度,LC50)值,而TEST软件还能预测理化参数。此外,TOPKAT特有的最佳预测区间能提示预测结果的正确性[10]。TEST软件则提供了不同的预测模型,弥补了单一预测方法的局限性。TEST和TOPKAT软件还能提供分子描述符的结构及其毒性贡献值、相似指数等,以此提高预测的正确性。
毒性预测软件的使用前提是分子二维结构的有效输入和兼容。简化分子线性输入规范(simplified molecular input line entry specification,SMILES)能快速便捷地将待测化学物的结构转换成计算机能识别的符号进行输入,并解决了软件兼容的问题[11-12]。本文采用SMILES输入法,结合TOPKAT[13]、TEST[14]两款毒性预测软件,对欧洲化学品管理署公布的321种化学物的健康及生态毒性风险进行预测,并将预测结果与毒理学数据进行比较,归纳软件的可预测性和适用范围。
1. 材料与方法
1.1 材料
以欧洲化学品管理署正式公布的具有代表性的有机磷类、氨基甲酸酯类和拟除虫菊酯类农药,苯系化学物,杂环类化学物,腈类化学物,酯类化学物,醇类化学物等321种化学物作为测试对象。
1.2 方法
1.2.1 简化分子线性输入规范
简化分子线性输入规范(SMILES)是一种利用美国信息交换标准代码(American standard code for information interchange,ASCII)字符串明确描述分子三维化学结构和化学反应的规范。SMILES最初由Weininger等于20世纪80年代后期提出[15],仅需简单的原子符号、键符号和语言规则就能完成分子结构的表达,因此SMILES是一种高效便捷的语言。SMILES所表述的分子结构式还能为其他化学智能软件表述化学物的信息,迄今为止,SMILES是应用最广泛、兼容性最好的线性编码。
SMILES基本规则中,氢原子是忽略不计的,芳环结构采用链打开或由凯库勒形式表达。表达时,被拆分的链端原子用数字标记,支链写在小括号里。SMILES编码的基本原则由五个要素构成,分别为原子、化学键、支链、闭环和未连接。SMILES表达中,环状结构需断开一个化学键来表述分子结构。连接键可按任意顺序标注,键断裂处的原子后面用数字标注。环己烷就是典型的例子,其SMILES表达为C1CCCCC1。而苯的SMILES表达为c1ccccc1,以小写字母表示。而四面体中心采用元素符号加“@”或“@@”来简化手性说明。符号“@”指相邻基团绕中心原子呈逆时针顺序排列。符号“@@”指相邻基团绕中心原子呈顺时针顺序排列。化学物的同分异构体遵循同分异构体简化线性输入规范(isomeric SMILES)编码规则。SMILES保证每种化学物分子只有唯一的SMILES表达式。
1.2.2 毒性预测软件
化学物毒性预测系统可分为两类:1)基于数据统计的专家系统;2)基于知识的专家系统。目前大多数毒性预测专家系统都是基于QSAR模型,建立化学物的分子结构与生物学活性(如潜在毒性)的相关性数学模型。构成QSAR模型的三个部分包括:1)一系列相关化学物的生物学和毒理学数据;2)这些化学物的理化性质数据;3)将上述两类数据通过统计分析方法相关联,最终建立化学结构与毒性效应量化关系的QSAR模型,用于毒性预测[16]。这就是基于数据统计的专家系统,如毒性预测软件TOPKAT,CASE/MultiCase等。基于知识的专家系统则利用系统的知识库来预测化学物的潜在毒性,而知识库中的规则源于专家的知识和可靠的毒理学实验数据,如毒性预测软件DEREK,OncoLogic,Hazard Expert,COMPACT等[17]。以下介绍本文涉及的两大软件。
1)TEST软件。TEST软件(Toxicity Estimation Software Tool)由美国环境保护总署设计并开发,通过大量的数据处理来识别目标结构中的有毒基团。TEST软件的数据库包含13种778个分子描述符,描述符的参数由实验数据和理论计算得到。TEST软件通过分析已知的化学物毒性数据并建立QSAR模型来预测化学物的毒性和每个描述符的使用及其相应的贡献值等。用户可根据自身需要选择适用的模型方法,如层析法、弹性判别分析法、单一模型法、官能团贡献法、相邻法和集成法。在分子结构输入方面,TEST软件可通过SMILES进行分子结构的转化输入,或者通过画图等方法,还可通过CAS号输入。在预测终点方面,TEST软件能预测健康、生态毒理数据,还能预测部分理化参数,包括7个毒性终点模型和7个理化终点模型,例如96 h呆头黑鱼50%致死浓度(LC50)值、48 h大型蚤50%效应浓度(EC50)值、大鼠口服50%致死剂量(LD50)值等。此外,TEST软件还能对每次预测的相似物进行分析,给出相似物的结构式、相似指数、实验数值和预测值。
2)TOPKAT软件。TOPKAT(Toxicity Prediction by Computer Assisted Technology)是以数据统计为基础的专家系统,以大量文献资料的毒理学信息作为数据基础,加以分析和计算后建立QSAR模型来预测化学物的健康、生态毒理学数据。在分子结构输入方面,TOPKAT软件可通过SMILES进行分子结构的转化输入,或者通过画图等方法,但是TOPKAT不支持CAS号输入。在预测终点方面,TOPKAT软件自带多个模块,能预测多种急性或慢性毒理作用和毒性数据,包括致癌性、致突变性、致畸性、皮肤致敏性、皮肤刺激性、眼刺激性、NTP啮齿类动物的致癌性、大鼠口服LD50值、大鼠吸入LC50值、呆头黑鱼LC50值、大型蚤EC50值等。TOPKAT软件还能给出最佳预测区间,可用于确定分子结构式的毒性是否在模型最佳预测区间内。TOPKAT软件还可进行相似性分析,并给出相似性指数以及相似物的具体数据和数据来源。
1.2.3 预测方法
化学物的毒性预测分为3个步骤,第一步采用SMILES描述化学结构,第二步将SMILES表达式输入TOPKAT、TEST两款毒性预测软件,生成分子二维结构后,选取TOPKAT软件的分子碎片常数模型和TEST软件的集成模型对化学物的健康和生态毒性进行预测。最后,选择大鼠口服毒性LD50(单位mg/kg)和鱼类急性毒性LC50-log(单位1/mol)作为预测终点,并获取预测结果。采用线性回归法分析结果的拟合度,以P<0.05为差异有统计学意义。通过将预测结果与欧洲化学品管理署公布的毒理学数据进行比较和分析,总结两种预测软件对于不同类型化学物的可预测性和适用范围。
2. 结果与分析
2.1 健康毒性预测结果
两款软件预测有机磷类、氨基甲酸酯类和拟除虫菊酯类农药、苯系化学物、杂环类化学物、酯类化学物、醇类化学物的健康毒性的结果与文献值比较接近。见表 1。以大鼠口服毒性LD50 > 300 mg/kg作为不归类为具有健康毒性的判断标准,对于所研究的161种化学物,除杂环类化学物外,以TOPKAT和TEST软件预测结果作为判断化学物是否归类为有毒品的平均正确率达到了80% ~ 93%。见表 2。总体上看,TEST软件适用于更多的化学物,其整体覆盖率较高,能够预测多取代苯环结构、杂环结构和大分子结构。而TOPKAT软件存在局限性,无法预测吡啶类、部分苯酚类和苯胺类化学物的毒性,而且对于超过105个非氢原子的分子、超过9个环的分子、超过10个碎片结构的分子、杂芳族和具有4个或4个以上多取代的单苯环结构,因为没有预测子模型,所以无法预测这些结构的毒性,如表 1中最后两种化学物。此外,TOPKAT软件的预测结果偏保守,对于161种所研究的化学物,TEST软件预测的健康毒性值有80%以上大于TOPKAT软件的预测值。
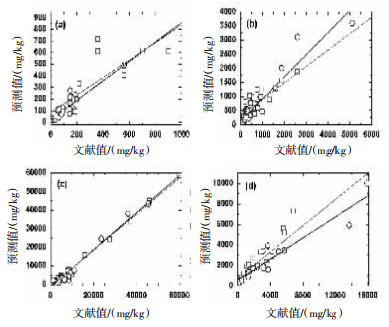
表 1 代表性化学物的SMILES表达式及其大鼠口服毒性LD50文献值和预测值(mg/kg)化学物名称 SMILES表达式 文献值 TOPKAT预测值 TEST预测值 农药 二溴磷 BrC(Cl)(Cl)C(Br)OP(=O)(OC)OC 92 126.0 98.35 萘肽磷 c1ccc3c2c1C=CC=C2C (=O)N (OP (=O) (OCC) OCC)C3(=O) 70 233.0 86.74 脱叶磷 CCCCSP(=O)(SCCCC)SCCCC 150 161.3 221.98 苯系物 邻氯苯亚甲基丙二腈 c1cccc(Cl)c1C=C(C#N)C#N 178 134.7 165.00 对硝基苯胺 c1cc(N) ccc1N(=O)=O 750 889.5 1 231.04 对苯二酚 c1cc(O) ccc1O 320 514.3 456.84 酯类 苯乙酸乙酯 c1ccccc1CC(=O)OCC 3 300 2 100.0 2 722.03 甲苯二异氰酸酯 c1cc(C) c(N=C=O) cc1N=C=O 5 110 3 600.0 4 164.35 乙酸丙酯 CC(=O)OCCC 9 370 6 500.0 5 050.52 杂环类 3-[[(2S, 4S)-4-[4-(3-甲基-1-苯基-1H-吡唑-5-基)-1-哌嗪基]-2-吡咯烷基]甲酰基]噻唑烷 CC1=NN(C(=C1)N1CCN(CC1)[C@@H]1CN[C@@H](C1)C(=O)N1CCSC1)C1=CC=CC=C1 > 500 预测无效 886.81 3-(4,4,5,5-四甲基-1,3,2-二氧杂环戊硼烷-2-基)环戊-2-烯-1-酮 C1CC(=O)C=C1B2OC(C)(C)C(C)(C)O2 > 2000 预测无效 4200.00 表 2 两种软件健康毒性预测结果比较化学物 种数 预测准确率/% 同文献值间的决定系数a TOPKAT TEST TOPKAT TEST 农药 34 86 80 0.852 0.659 苯系物 31 87 88 0.895 0.932 酯类 32 89 90 0.971 0.986 醇类 33 91 93 0.854 0.891 杂环类 31 66 70 0.673 0.782 [注] a决定系数所对应P值均<0.05 两款软件预测的161类化学物的健康毒性值与文献值的线性相关性良好,且每对数据较接近。TOPKAT软件预测农药类化学物的结果优于TEST软件,然而,TEST软件预测苯系、酯类和醇类化学物的结果优于TOPKAT软件。TOPKAT、TEST软件预测的大鼠口服毒性LD50值与文献值之间存在显著的相关性,TEST软件预测健康毒性的正确率略高于TOPKAT软件。而两款软件对于杂环类化学物的预测正确率不是很高。TOPKAT和TEST软件预测大鼠口服毒性LD50值与文献值回归直线图及预测结果比较见表 2、图 1。
2.2 生态毒性预测结果
除了能预测健康毒性外,TOPKAT、TEST软件还能预测生态毒性。两款软件预测结果与文献值比较接近。见表 3。TOPKAT、TEST软件能覆盖绝大部分化学物的生态毒性预测,以鱼类96 h LC50 > 1 mg/L作为不归类为具有水生急性毒性的判断标准,对于所研究的160种化学物,以TOPKAT和TEST软件预测结果作为判断化学物是否归类为环境有毒品的平均正确率达到了75% ~ 97%。见表 4。相比于TEST软件,TOPKAT软件在预测部分化学物生态毒性时优势较为明显,尤其是针对农药类化学物时。对于苯系、酯类和醇类化学物,两款软件的生态毒性预测结果比较接近。见表 3和表 4。
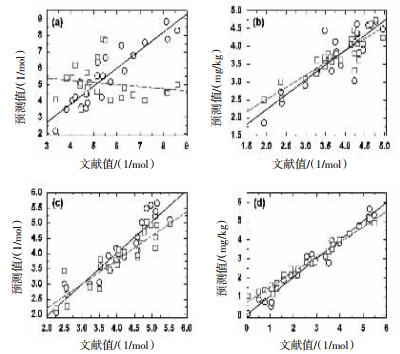
表 3 代表性化学物的SMILES表达式及其鱼类急性毒性LC50-log文献值和预测值(1/mol)化学物名称 SMILES表达式 文献值 TOPKAT预测值 TEST预测值 农药 丙溴磷 c1cc(Br)cc(Cl)c1OP(= O)(OCC)SCCC 6.32 5.85 6.19 保棉磷 c1cccc2c1N=NN(CSP (=S)(OC)OC)C2(=O) 5.51 6.64 5.11 氰戊菊酯 c1cc(Cl)ccc1C(C(C)C) C(=O)OC(C#N)c2cc (Oc3ccccc3 ccc2 8.12 8.83 8.22 苯系物 苯酚 c1ccccc1O 3.49 3.56 3.45 苯胺 c1ccccc1N 2.99 2.90 3.09 N/N-二羟乙基苯胺 c1ccccc1N(CCO) CCO 2.39 2.41 2.53 酯类 苯甲酸乙酯 c1ccccc1C(=O) OCC 4.24 4.12 3.80 甲基丙烯酸苄基酯 c1ccccc1COC(=O) C(= C)C 4.58 4.59 4.57 丁酸乙烯酯 CCCC(=O)OC=C 3.98 4.18 3.76 醇类 2-吗啉乙醇 C1COCCN1CCO 1.68 1.42 1.46 叔丁醇 CC(C)(C)O 1.06 0.70 1.43 正戊醇 CCCCCO 2.21 2.40 2.44 表 4 两种软件生态毒性预测结果比较化学物 种数 预测准确率/% 同文献值间的决定系数a TOPKAT TEST TOPKAT TEST 农药 31 92 75 0.826 0.493 苯系物 32 95 97 0.746 0.787 酯类 32 94 88 0.890 0.821 醇类 33 92 94 0.965 0.981 杂环类 32 87 90 0.732 0.829 [注]a决定系数所对应P值均 < 0.05 两款软件预测的160种化学物鱼类急性毒性LC50值与文献值之间的线性相关性良好,且每对数据较接近。TOPKAT软件预测农药类、酯类化学物的鱼类急性毒性LC50结果优于TEST软件[见图 2(a)、(c)],而TEST软件预测苯系和醇类化学物的鱼类急性毒性LC50结果优于TOPKAT软件[见图 2(b)、(d)]。
综上所述,TOPKAT和TEST毒性预测软件对农药类、苯系、酯类、醇类等化学物的健康和生态毒性的预测结果较好。相对而言,TOPKAT软件对于农药类化学物的健康和生态毒性预测正确率高于TEST软件,而TEST软件对于苯系化学物的毒性预测结果略优于TOPKAT软件。对于具有单一官能团结构的酯类和醇类化学物,TOPKAT和TEST软件都显示出优越的预测能力。对于化学结构复杂的杂环类化学物,TOPKAT和TEST软件的毒理学预测结果都不是很理想。这是因为,TOPKAT和TEST软件的毒性预测都是建立在化学结构与毒性定量构效关系的基础上的,复杂结构的化学物具有多个基团和结构碎片,这些基团和结构碎片的毒理学贡献值难以定量分析,其毒性叠加效应难以具体计算,为毒性预测带来了困难。
3. 讨论
SMILES能简化化学物的分子结构表达,且与多种毒性预测软件有良好的兼容性。TOPKAT和TEST软件都能预测绝大多数的常见化学物,TEST软件的化学物预测覆盖率高于TOPKAT软件。两种毒性预测软件的正确率约在80% ~ 90%左右,321种化学物中,约有80%的化学物毒性经TEST软件预测的毒性预测结果大于TOPKAT软件预测值。农药类化学物首选TOPKAT软件进行毒性预测,苯系化学物优先考虑使用TEST软件进行毒性预测。在其余化学物的应用中,可以结合两种毒性预测软件的结果,综合评估化学物的毒性。今后随着计算机技术、信息科学和毒理学理论的发展,更多优化的毒性预测软件会应用到药物毒理学评价和化学品分类鉴别中。例如,DEREK软件公司最新开发了优化的毒性软件METEOR,增加了专家系统预测化学物代谢产物和代谢路径等功能,而Hazard Expert软件则能预测给药途径、用药剂量和时程等信息。未来更多智能化多功能的模拟软件将为新药早期毒性筛选和化学物危险性预判提供依据,不断推动药物毒理学、药理学和生理学领域研究。
-
表 1 代表性化学物的SMILES表达式及其大鼠口服毒性LD50文献值和预测值(mg/kg)
化学物名称 SMILES表达式 文献值 TOPKAT预测值 TEST预测值 农药 二溴磷 BrC(Cl)(Cl)C(Br)OP(=O)(OC)OC 92 126.0 98.35 萘肽磷 c1ccc3c2c1C=CC=C2C (=O)N (OP (=O) (OCC) OCC)C3(=O) 70 233.0 86.74 脱叶磷 CCCCSP(=O)(SCCCC)SCCCC 150 161.3 221.98 苯系物 邻氯苯亚甲基丙二腈 c1cccc(Cl)c1C=C(C#N)C#N 178 134.7 165.00 对硝基苯胺 c1cc(N) ccc1N(=O)=O 750 889.5 1 231.04 对苯二酚 c1cc(O) ccc1O 320 514.3 456.84 酯类 苯乙酸乙酯 c1ccccc1CC(=O)OCC 3 300 2 100.0 2 722.03 甲苯二异氰酸酯 c1cc(C) c(N=C=O) cc1N=C=O 5 110 3 600.0 4 164.35 乙酸丙酯 CC(=O)OCCC 9 370 6 500.0 5 050.52 杂环类 3-[[(2S, 4S)-4-[4-(3-甲基-1-苯基-1H-吡唑-5-基)-1-哌嗪基]-2-吡咯烷基]甲酰基]噻唑烷 CC1=NN(C(=C1)N1CCN(CC1)[C@@H]1CN[C@@H](C1)C(=O)N1CCSC1)C1=CC=CC=C1 > 500 预测无效 886.81 3-(4,4,5,5-四甲基-1,3,2-二氧杂环戊硼烷-2-基)环戊-2-烯-1-酮 C1CC(=O)C=C1B2OC(C)(C)C(C)(C)O2 > 2000 预测无效 4200.00 表 2 两种软件健康毒性预测结果比较
化学物 种数 预测准确率/% 同文献值间的决定系数a TOPKAT TEST TOPKAT TEST 农药 34 86 80 0.852 0.659 苯系物 31 87 88 0.895 0.932 酯类 32 89 90 0.971 0.986 醇类 33 91 93 0.854 0.891 杂环类 31 66 70 0.673 0.782 [注] a决定系数所对应P值均<0.05 表 3 代表性化学物的SMILES表达式及其鱼类急性毒性LC50-log文献值和预测值(1/mol)
化学物名称 SMILES表达式 文献值 TOPKAT预测值 TEST预测值 农药 丙溴磷 c1cc(Br)cc(Cl)c1OP(= O)(OCC)SCCC 6.32 5.85 6.19 保棉磷 c1cccc2c1N=NN(CSP (=S)(OC)OC)C2(=O) 5.51 6.64 5.11 氰戊菊酯 c1cc(Cl)ccc1C(C(C)C) C(=O)OC(C#N)c2cc (Oc3ccccc3 ccc2 8.12 8.83 8.22 苯系物 苯酚 c1ccccc1O 3.49 3.56 3.45 苯胺 c1ccccc1N 2.99 2.90 3.09 N/N-二羟乙基苯胺 c1ccccc1N(CCO) CCO 2.39 2.41 2.53 酯类 苯甲酸乙酯 c1ccccc1C(=O) OCC 4.24 4.12 3.80 甲基丙烯酸苄基酯 c1ccccc1COC(=O) C(= C)C 4.58 4.59 4.57 丁酸乙烯酯 CCCC(=O)OC=C 3.98 4.18 3.76 醇类 2-吗啉乙醇 C1COCCN1CCO 1.68 1.42 1.46 叔丁醇 CC(C)(C)O 1.06 0.70 1.43 正戊醇 CCCCCO 2.21 2.40 2.44 表 4 两种软件生态毒性预测结果比较
化学物 种数 预测准确率/% 同文献值间的决定系数a TOPKAT TEST TOPKAT TEST 农药 31 92 75 0.826 0.493 苯系物 32 95 97 0.746 0.787 酯类 32 94 88 0.890 0.821 醇类 33 92 94 0.965 0.981 杂环类 32 87 90 0.732 0.829 [注]a决定系数所对应P值均 < 0.05 -
[1] MYINT K Z, WANG L, TONG Q, et al. Molecular fingerprint-based artificial neural networks QSAR for ligand biological activity predictions[J]. Mol Pharmaceutics, 2012, 9(10):2912-2923. doi: 10.1021/mp300237z
[2] WANG M J, ZHAO X B, WU D, et al. Design, synthesis, crystal structure, insecticidal activity, molecular docking, and QSAR studies of novel N3-substituted imidacloprid derivatives[J]. J Agric Food Chem, 2014, 62(24):5429-5442. doi: 10.1021/jf501108j
[3] CHERKASOV A, MURATOV E N, FOURCHES D, et al. QSAR modeling:Where have you been where are you going to[J]. J Med Chem, 2014, 57(12):4977-5010. doi: 10.1021/jm4004285
[4] US Environmental Protection Agency. Operation manual for the ecological structure-activity relationship model (ECOSAR) class program (Version 1.1)[A]. 2011.
[5] 程艳, 陈会明, 于文莲. QSAR技术对高关注化学物质生态环境毒理风险预测[J].环境科学研究, 2009, 22(7):817-822. http://d.old.wanfangdata.com.cn/Periodical/hjkxyj200907014 [6] SNYDER R D, PEARL G S, MANDAKAS G, et al. Assessment of the sensitivity of the computational programs DEREK, TOPKAT, and MCASE in the prediction of the genotoxicity of pharmaceutical molecules[J]. Environ Mol Mutagen, 2004, 43(3):143-158. doi: 10.1002/em.20013
[7] BARRATT M D, CASTELL J V, MIRANDA M A, et al. Development of an expert system rulebase for the prospective identification of photoallergens[J]. J Photochem Photobiol B, 2000, 58(1):54-61. doi: 10.1016/S1011-1344(00)00100-7
[8] HILLEBRECHT A, MUSTER W, BRIGO A, et al. Comparative evaluation of in silico systems for ames test mutagenicity prediction:Scope and limitations[J]. Chem Res Toxicol, 2011, 24(6):843-854. doi: 10.1021/tx2000398
[9] 黄晓龙.国外化学物结构-毒性数据库"TOPKAT"简介[J].中国新药杂志, 2005, 14(3):262-264. doi: 10.3321/j.issn:1003-3734.2005.03.003 [10] 秦涛余, 刘东武, 陈志伟. Topkat 6.2软件对斑蜇素衍生物结构-毒性关系的分析研究[J].生命的化学, 2009, 28(1):124-128. http://www.cnki.com.cn/Article/CJFDTotal-SMHX200901032.htm [11] KARWATH A, DE R L. SMIREP:Predicting chemical activity from SMILES[J]. J Chem Inf Model, 2006, 46(6):2432-2444. doi: 10.1021/ci060159g
[12] BONE R G A, FIRTH M A, SYKES R A. SMILES extensions for pattern matching and molecular transformations:applications in chemoinformatics[J]. J Chem Inf Comput Sci, 1999, 39(5):846-860. doi: 10.1021/ci990422w
[13] VENKATAPATHY R, MOUDGAL C J, BRUCE R M. Assessment of the oral rat chronic lowest observed adverse effect level model in TOPKAT, a QSAR software package for toxicity prediction[J]. J Chem Inf Comput Sci, 2004, 44(5):1623-1629. doi: 10.1021/ci049903s
[14] US Environmental Protection Agency. User's Guide for T.E.S.T. (version 4.0) (Toxicity Estimation Software Tool)[A]. 2011.
[15] WEININGER D, WEININGER A, WEININGER J L. Algorithm for generation of unique SMILES notation[J]. J Chem Inf Comput Sci, 1989, 29(2):97-101. http://database.oxfordjournals.org/external-ref?access_num=10.1021/ci00062a008&link_type=DOI
[16] YOST E E, STANEK J, DEWOSKIN R S, et al. Estimating the potential toxicity of chemicals associated with hydraulic fracturing operations using quantitative structure-activity relationship modeling[J]. Environ Sci Technol, 2016, 50(14):7732-7742. doi: 10.1021/acs.est.5b05327
[17] BHHATARAI B, WILSON D M, PARKS A K, et al. Evaluation of TOPKAT, toxtree, and derek nexus in silico models for ocular irritation and development of a Knowledge-based framework to improve the prediction of severe irritation[J]. Chem Res Toxicol, 2016, 29(5):810-822. doi: 10.1021/acs.chemrestox.5b00531
-
期刊类型引用(4)
1. 戴聪,田珩,吴纯敏,杨仪雪,贝琦华,严全鸿. 丙酸倍氯米松吸入气雾剂中新杂质的定性定量分析. 药学前沿. 2024(11): 416-423 .  百度学术
百度学术
2. 贺泳迪,宋金瓯,武斌,王晓文,谢继标,王斌. 应用毒性评价软件工具和Toxtree软件预测硝基烃及其衍生物的毒性. 中国药理学与毒理学杂志. 2022(07): 509-520 .  百度学术
百度学术
3. 韩中惠,王晓敏,张燕,刘冰,王硕. 应用Discovery Studio(TOPKAT)软件预测糖抑制PhIP过程中新产物的毒理学性质. 中国食品学报. 2020(10): 247-253 .  百度学术
百度学术
4. 王思怿,范宾,董学胜. 简化分子线性输入规范介绍及其化学品毒性预测效果回顾. 职业卫生与应急救援. 2018(05): 471-476 .  本站查看
本站查看
其他类型引用(15)





 下载:
下载: